近期,我校闫喜武教授科研团队完成了菲律宾蛤仔全基因组图谱绘制,并通过转录组测序和对不同组织和发育阶段的RNA测序分析,对缺氧、酸化和寄生虫应激适应的分子基础开展了深入研究并取得重大进展。研究成果于近日以“Clam genome sequence clarifies the molecular basis of its benthic adaptation and extraordinary shell color diversity”为题发表在国际著名期刊《Cell》子刊《iScience》上。闫喜武教授和聂鸿涛副研究员为本文的共同通讯作者,该文章为我校首次以第一作者和通信作者单位在iScience上发表的研究论文。
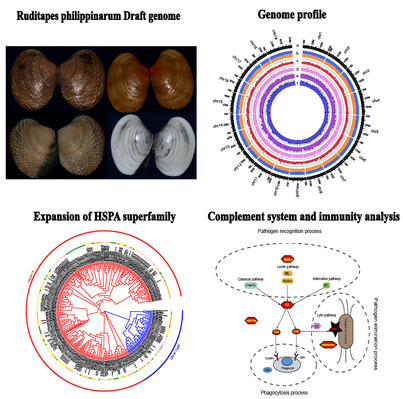
菲律宾蛤仔 (Ruditapes philippinarum)是我国四大养殖贝类之一,也是我国单种产量最高的养殖贝类,年产量300多万吨,占世界养殖产量的90%以上。近年来,我国蛤仔苗种生产和增养殖规模不断扩大,经济和社会效益显著,然而其种质质量下降、存活率低等问题日趋严重。蛤仔基因组信息的匮乏成为我们理解其抗病、抗逆机制的障碍,破译蛤仔基因组信息、开展重要性状遗传改良成为当下的重要课题。该团队首次完成了高质量菲律宾蛤仔全基因组图谱的绘制,研究发现,菲律宾蛤仔基因组中有许多与免疫相关的基因家族发生扩张,表明免疫和抗应激相关基因的扩张可能在对不利环境的抵抗中发挥重要作用,并对蛤仔适应底泥中的埋栖生活产生深远影响。该项目完成的高质量菲律宾蛤仔全基因组图谱,为蛤仔抗病抗逆、生长发育等重要性状的遗传解析以及种质改良等相关研究提供了重要理论支撑。
《Cell》是与《Nature》《Science》并列的世界三大顶级期刊之一,《iScience》是《Cell》旗下继《Neuron》《Cell reports》《Aging cell》等专业子刊之后新创的综合性期刊,主要发表包括生命科学、物理学、地球学以及环境科学在内的创新性基础和应用研究。
论文连接:Clam genome sequence clarifies the molecular basis of its benthic adaptation and extraordinary shell color diversity
https://www.cell.com/iscience/fulltext/S2589-0042(19)30328-1
科技处 供稿
